通用功能
1. 注册和登录
首次使用Hermite®平台时,您需要注册账号。在浏览器地址栏中输入https://hermite.dp.tech,打开Hermite登录页面:
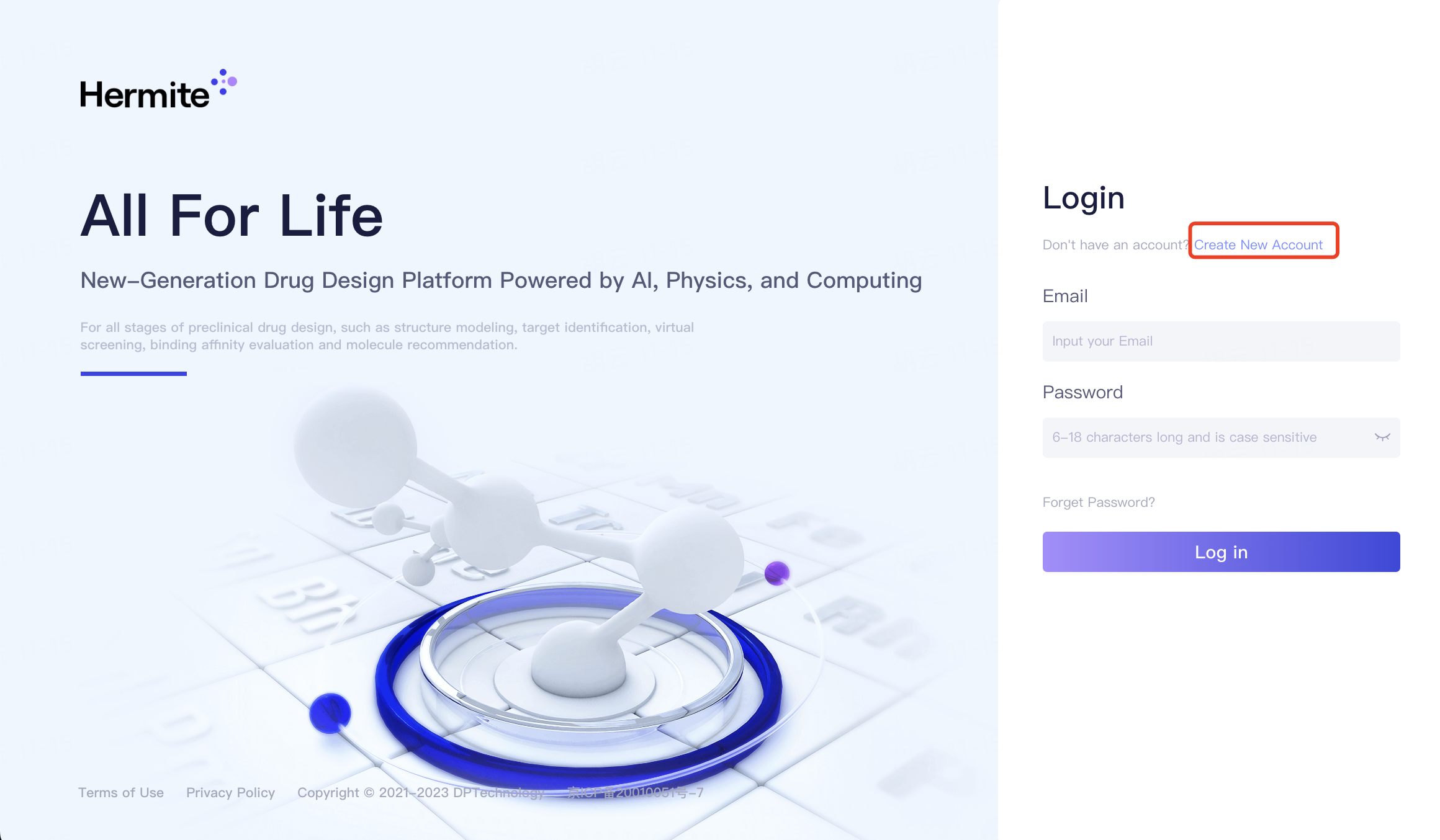
点击“Create New Accout”创建新帐号。输入注册Email地址后,点击“Get Verification Code”按钮获取注册验证码。此时系统会自动发送验证码到您的注册邮箱。
注:如果您在5分钟内��仍未收到验证码邮件,请先检查邮件是否被您的邮件系统识别为垃圾邮件。若确定未收到验证码邮件,可联系Hermite官方运营人员帮忙处理。
输入注册的手机号后,点击“Get Verification Code”按钮获取注册验证码,系统会自动发送验证码到您的手机短信中。
注:如果您在5分钟内仍未收到短信验证码,可联系Hermite官方运营人员帮忙处理。
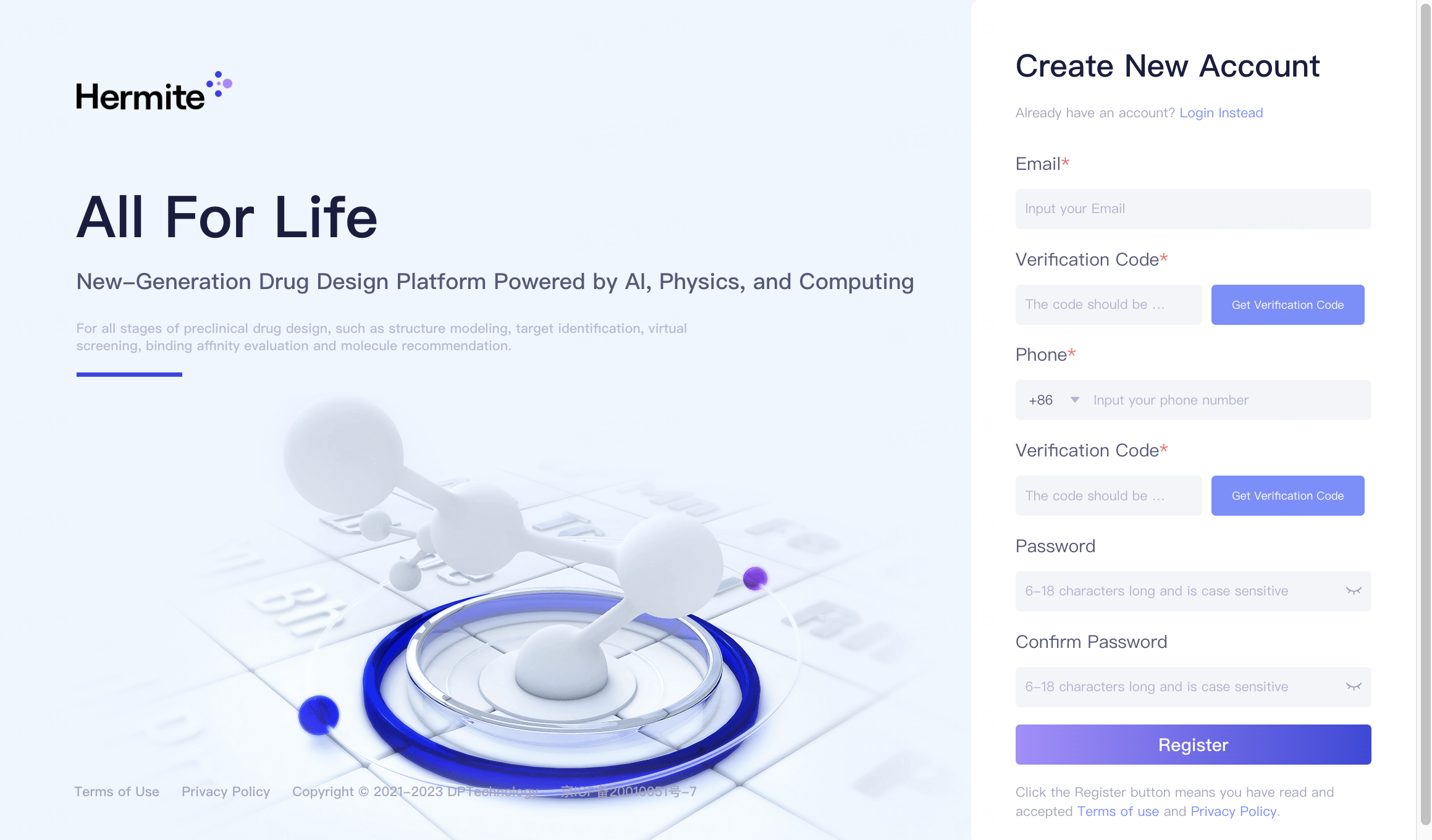
输入验证码和新的账户密码后,点击Register按钮完成新用户的注册。
2. 通用菜单栏
首次进入Herimite®平台,您会自动进入主界面,同时,Hermite®平台采用Project方式管理您的研究工作和计算任务。主界面包含Hermite®平台4大图形化窗口以及左侧通用菜单栏。左侧菜单栏的功能包括:
2.1 File
Import Structure
详见《图形化功能》部分。
Get PDB
详见《图形化功能》部分。
2.2 Function
| Structure Modeling | Protein Folding | 基于Uni-Fold从蛋白质序列出发,预测蛋白质结构 |
| EM Structure Fitting | 基于cryo-EM密度图的全原子结构模型柔性搭建工具 | |
| Loop Optimization | 蛋白柔性loop结构的构象优化 | |
| Virtual Screening | Docking | 基于GPU加速、Uni-Mol优化结合pose的分子对接程序 |
| Induced Fit Docking | 基于诱导契合理论的蛋白和配体的柔性对接 | |
| Virtual Screening Workflow | 整合Protein Preparation、Ligand Preparation、Docking和MM PB/GBSA,一站式完成超高通量虚筛 | |
| Binding Stability | 对蛋白-小分子复合物进行100 ns的全原子模拟以评估结合稳定性 | |
| Pharmacophore Generation & Screening | 基于药效团的虚拟筛选工具 | |
| Binding Affinity Evaluation | MM PB/GBSA Structure | 衡量配体和靶点的结合亲和力 |
| FEP Calculation | 基于自由能微扰理论、分子动力学模拟和高性能计算,评估一系列结构相近的候选药物分子(Ligands)与靶蛋白(Protein)的亲和力(Affinity)差异的工具 | |
| FEP Analysis | FEP Calculation 或 FEP Recalculation的结果分析工具 | |
| FEP Protein Mutation | 在FEP计算过程中,支持蛋白中的氨基酸发生Alchemical Transform变化,精确计算点突变对蛋白质性质的影响(目前仅开放了预测突变前后蛋白热稳定性差异的功能) | |
| Aquasite | 计算分析靶点口袋处水分子分布与稳定性 | |
| Biomacromolecule | Antibody Folding | 根据轻链和重链的序列进行抗体结构预测 |
| Sequence Alignment | 基于多序列比对算法(MSA)的蛋白质序列比对工具 | |
| Antibody Numbering | 基于抗体编号系统(支持:IMGT、Kabat、Chothia),对抗体序列的CDR区域进行标注的工具 | |
| Antibody Humanization | 基于数据库和统计模型,对抗体进行人源化改造的工具。支持CDR区标记和移植,人源抗体,并提供图形化功能进行抗体人源化改造 | |
| Antibody Properties | 基于数据库和统计模型,对抗体的可开发性(包括:粘度、聚集性、清除率、等电点、消光系数等)进行评估的工具,同时支持对抗体可变区(Fv)进行结构建模 | |
| Nanobody Properties | 基于数据库和统计模型,对纳米抗体的可开发性(包括:聚集性、清除率、等电点等)进行评估的工具 | |
| PTM Prediction | 基于人工智能算法,对蛋白质翻译后修饰(PTM)位点(例如:磷酸化、糖基化、泛素化、亚硝基化、甲基化、乙酰化等)进行预测的工具 | |
| Protein-Protein Docking | 基于快速傅里叶变换(FFT)算法的蛋白-蛋白刚性对接工具 | |
| Protein-Protein Interaction | 蛋白质与蛋白质之间的相互作用 | |
| AI Protein Mutation | 基于人工智能算法,融合蛋白质结构和动力学信息等多模态特征,快速预测蛋白质突变前后热稳定性差异的工具 | |
| Molecule Recommendation | VD-Gen | 基于虚拟动力学(Virtual Dynamics)人工智能算法,依赖蛋白口袋的分子从头设计功能 |
| Similar Molecules Search | 基于多种手段生成查询分子的分子指纹,匹配其和目标分子间的相似性 | |
| Substructure Search | 基于子结构的SMARTS匹配目标分子相同的部分 | |
| Maximum Common Substrucrture | 寻找一批分子中的最大公共子结构 | |
| Compound Clustering | 根据分子指纹将性质相似的分子聚集到一类中 | |
| Uni-QSAR | 基于人工智能(深度学习,机器学习)多种模型联合的定量构效关系(QSAR)建模和预测工具,并在分子1D和2D描述符的基础上,加入了基于分子3D结构预训练模型(Uni-Mol)的全新3D分子描述符,大大提高了QSAR模型的准确性 | |
| Uni-QSAR Analysis | Uni-QSAR模型性能比较与分析工具 | |
| General | Protein Preparation | 对蛋白进行处理以用于后续任务 |
| Ligand Preparation | 对配体进行处理以用于后续任务 | |
| Protein Alignment | 对蛋白质结构进行3D叠合(根据:backbone,Ca,sidechain)的工具,并支持多个蛋白结构的叠合操作 |
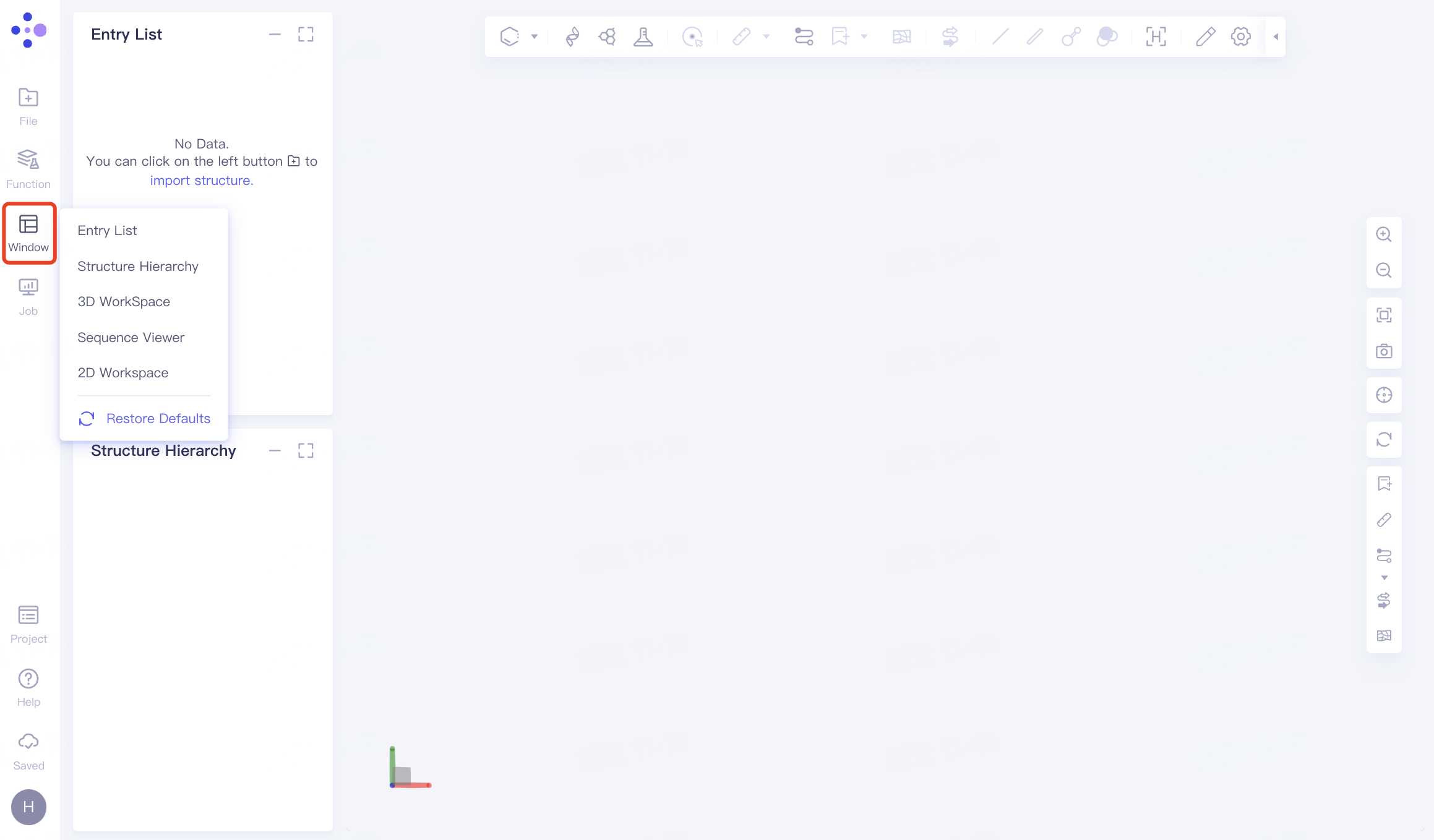
2.3 Windows
唤起Hermite平台常驻的窗口(任一图形化四组件)。
唤起您已经激活的功能(即,您使用过程中最小化的功能从这里再次进行)。
还原页面默认布局。
2.4 Job List
2.4.1 入口
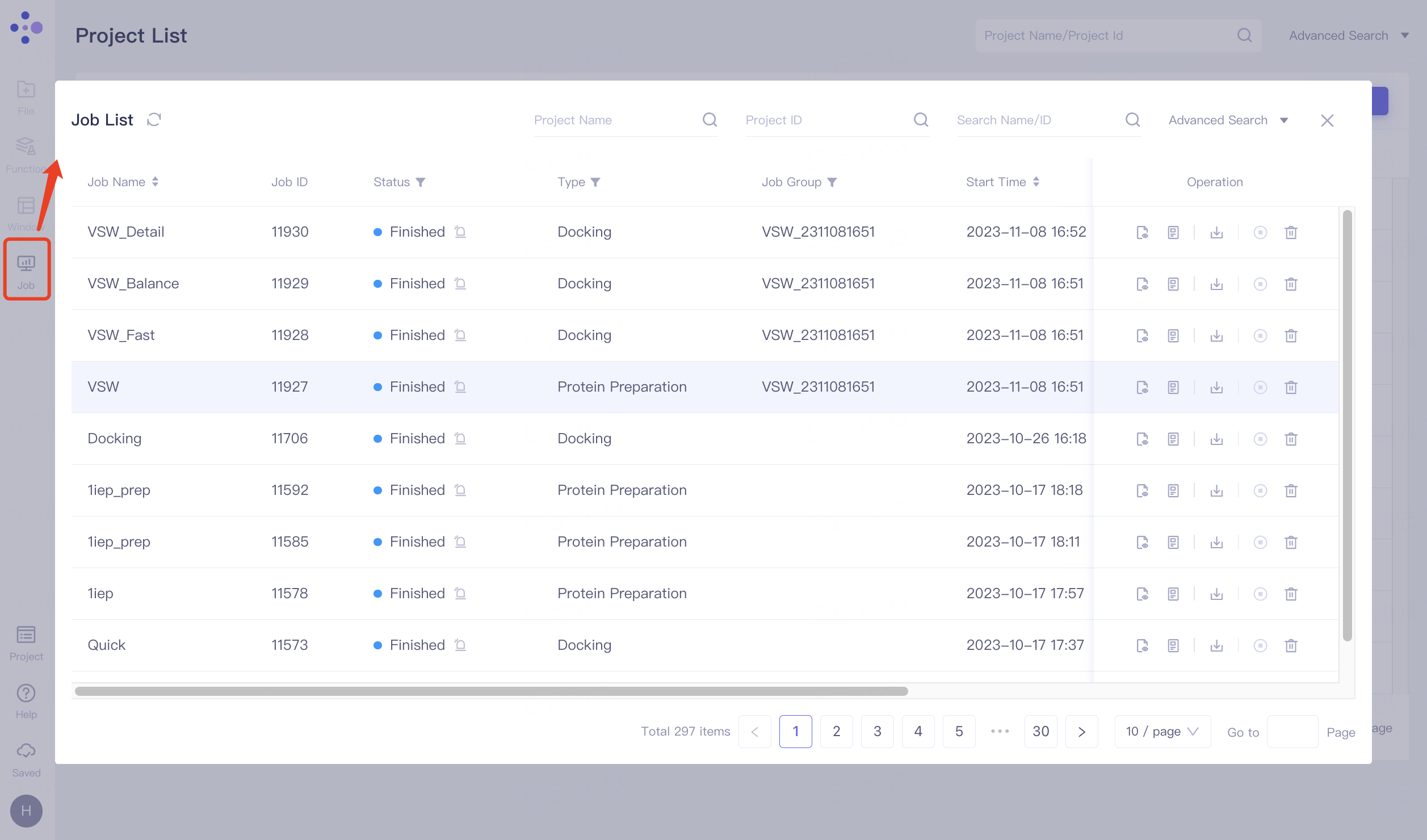
当您当前不在某个Project中时,点击左侧通用菜单栏“Job”,展开“Job List”界面,可以查看历史全部的Job;
当您当前在某个Project中时,点击左侧通用菜单栏“Job”,展开“Job List”界面,可以查看该Project下的全部Job。
2.4.2 操作
默认界面支持按照Project Name、Project ID以及Name/ID条件搜索;
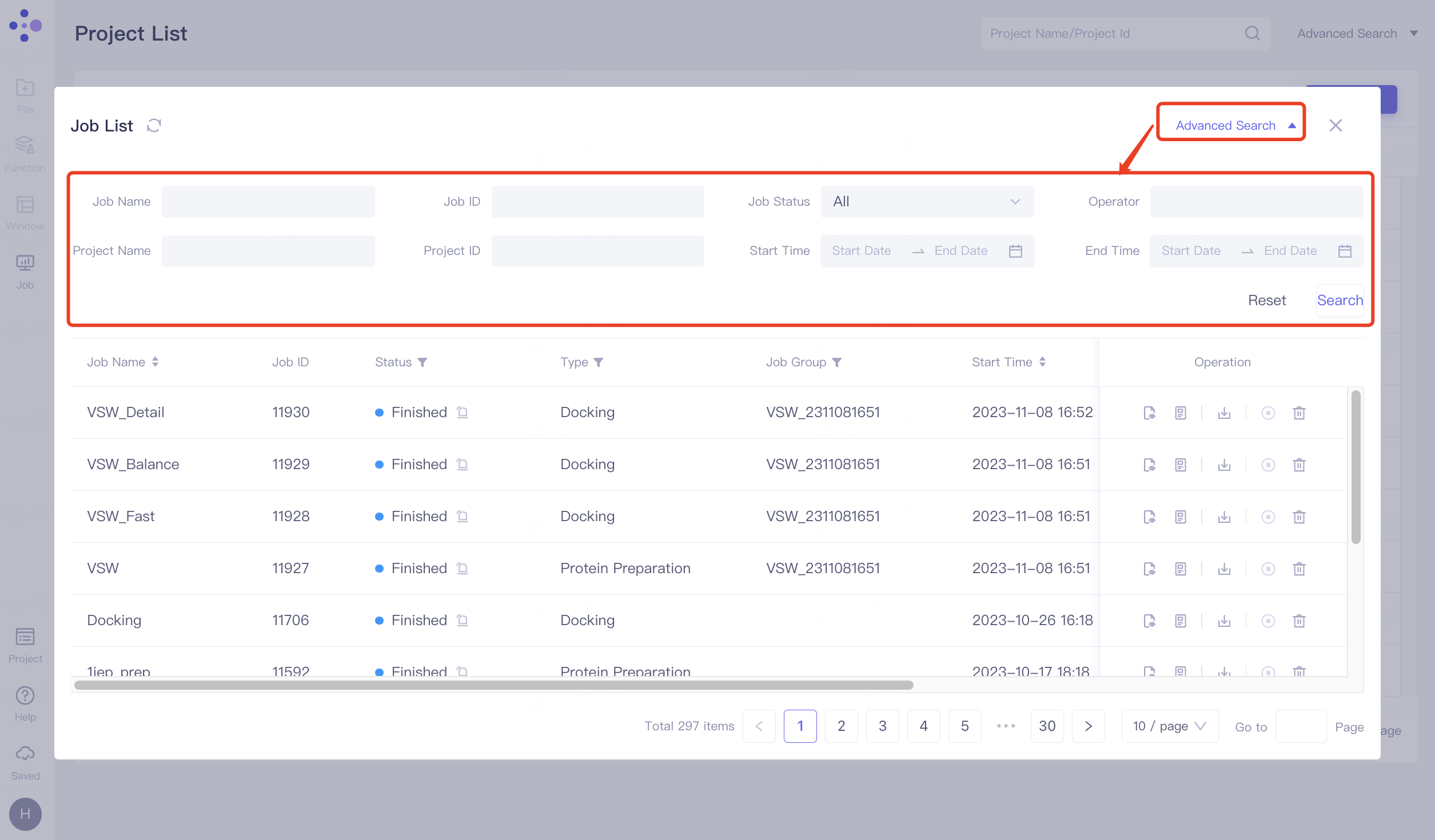
点击“Advanced Search”,展开高级搜索,支持按照Job Name、Job ID、Job Status、Operator、Project Name、Project ID、Start Time和End Time搜索,点击“Search”即可进行搜索,点击“Reset”重置搜索项。
支持按照Job Name、Job Status、Start Time和End Time进行排序。
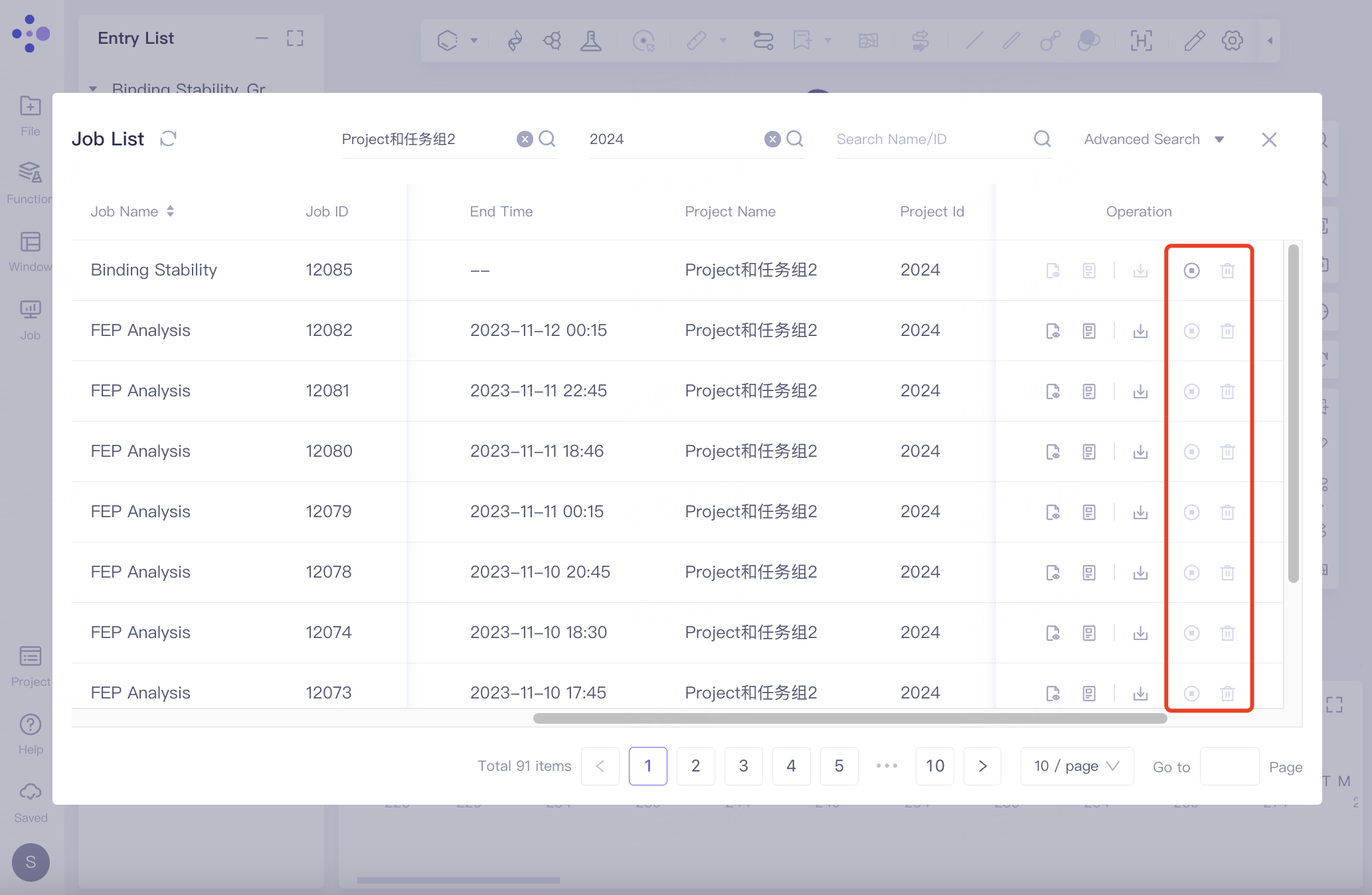
Operation下的操作:
Show:展示该Job的结果;
Log & Paramas:日志和参数,在您任务计算失败,需要寻求Hermite官方运营人员帮助时,一并提供的信息,便于我们快速帮您定位问题;
Download:下载该Job的相关文件;
Cancel:取消该任务,取消任务并非暂停,一旦取��消该任务后,如果需要再次运行,需要去Functions中重新计算;
Delete:删除该任务。
-
管理员与成员在Job List上支持的操作有差异,具体如下:
-
管理员与成员均可对自己的项目进行“Cancel”和“Delete”的操作;
-
管理员可对成员的项目进行“Cancel”和“Delete”的操作;
-
成员不可以对管理员的项目进行“Cancel”和“Delete”的操作。
-
2.5 Project
2.5.1 New Project
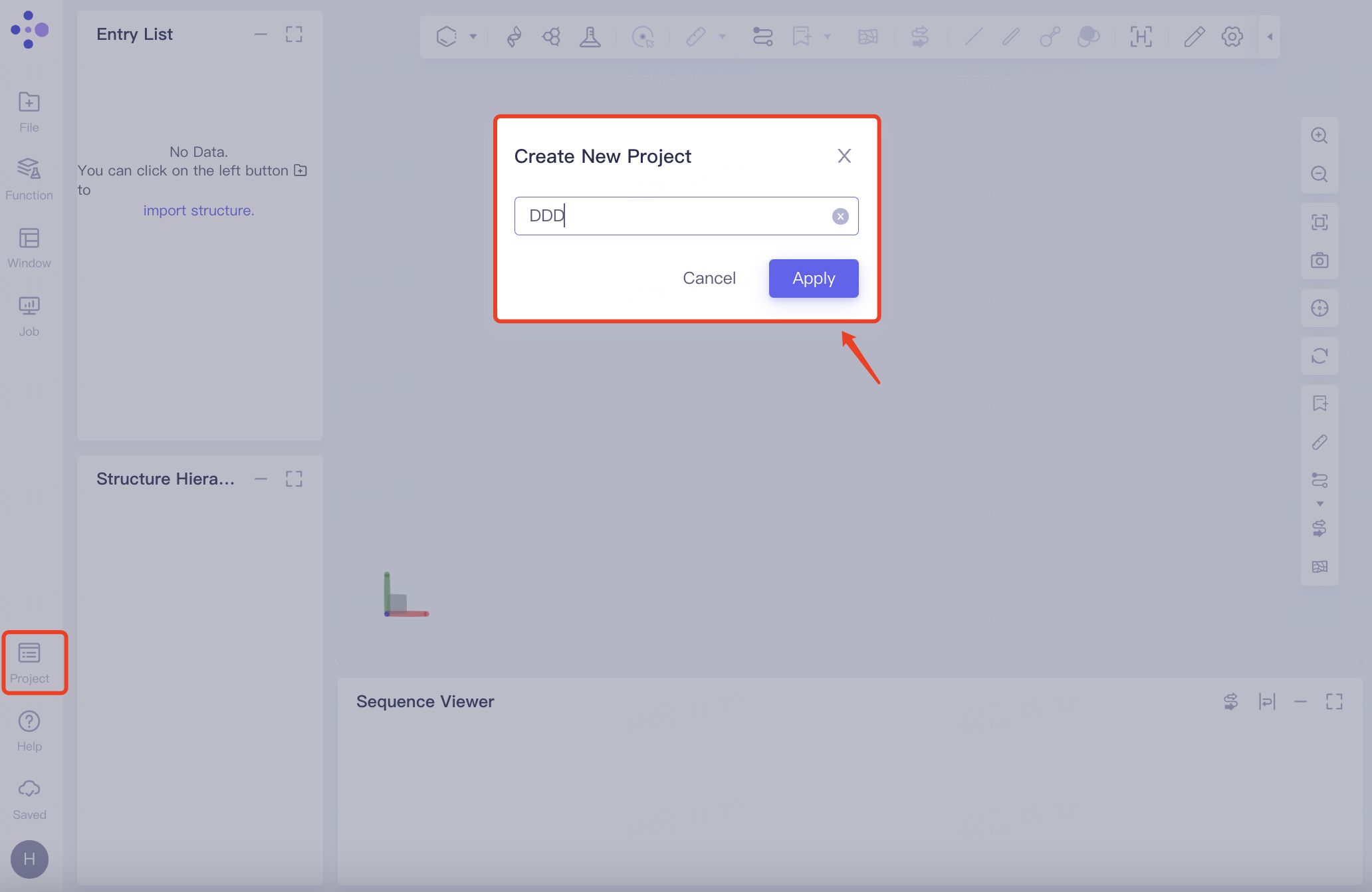
为新的研究计算体系创建独立的Project,具体步骤:通用工具栏Menu → Project → New Project → 命名新Project → 点击Apply → 自动跳转新页面(默认打开4大图形化窗口)。
当成员在受邀组织内时,新建项目自动与管理员同步。
 |  |
2.5.2 Save Project
手动保存当前Project下图形化界面的展示状态和各种激活功能的参数,具体步骤:通用工具栏Menu → Project → Save Project;或者快捷键方式:Ctrl+S(Win系统)/ Command+S(OSX系统)。
注:您进行重要操作后,希望您进行数据保存;同时,为了最大程度便捷您的工作,Hermite作为SaaS云平台,会定期自动保存您在本地浏览器的项目数据至您的云端账号。
2.5.3 Project List
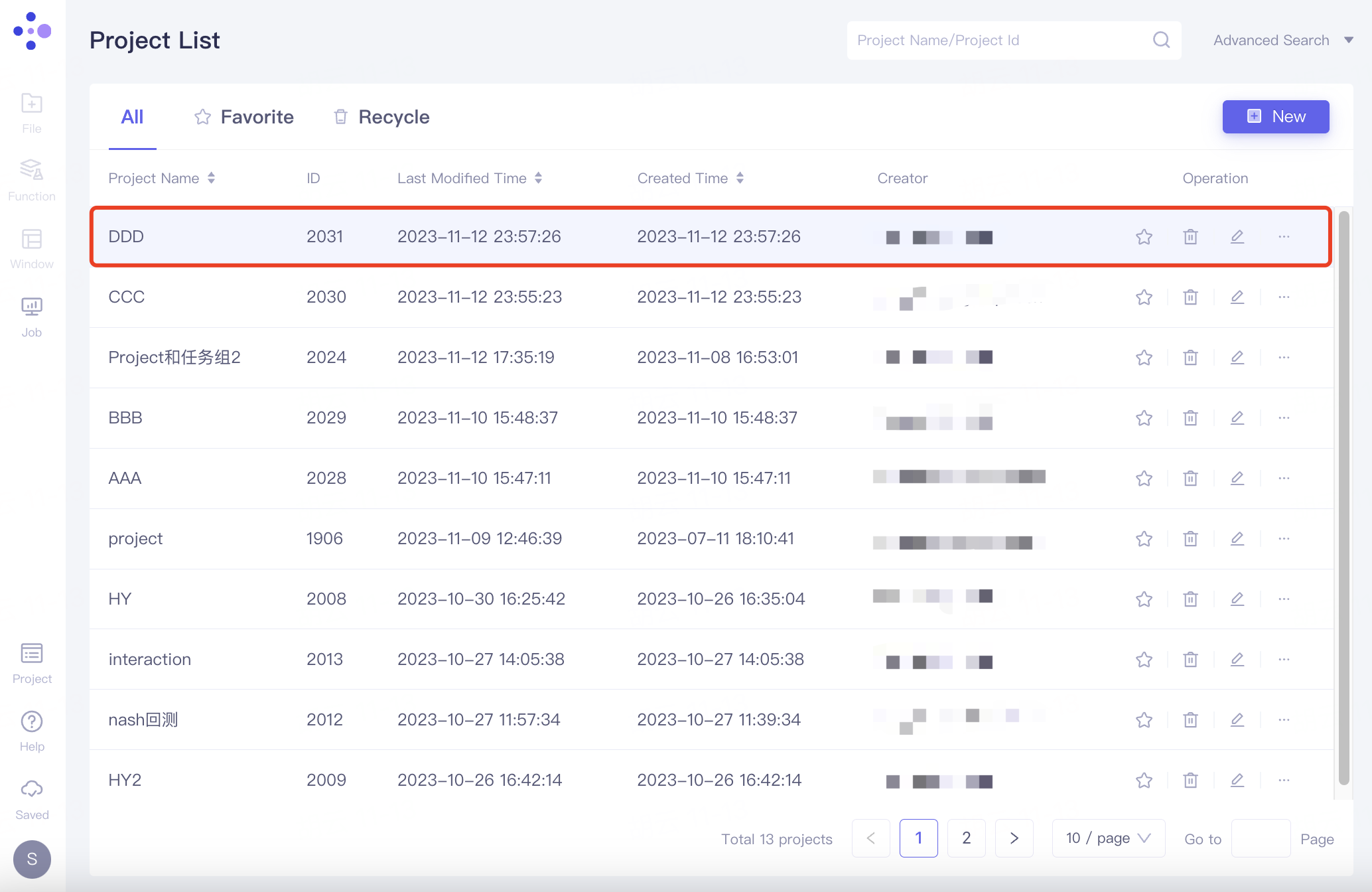
Project List 提供了您在Hermite平台的历史项目的全方位管理,支持通过点击Project Name列下的项目名进入该Project。
支持按Project Name、Last Modified Time、Create Time进行搜索和排序。
Operation下的操作:
Add to Favorite:收藏该项目,收藏的项目可在Favorite分类中查看;
Delete:删除该项目,删除的项目可在Recycle分类中查看;
Rename:对该项目重命名;
Member:添加组织成员。
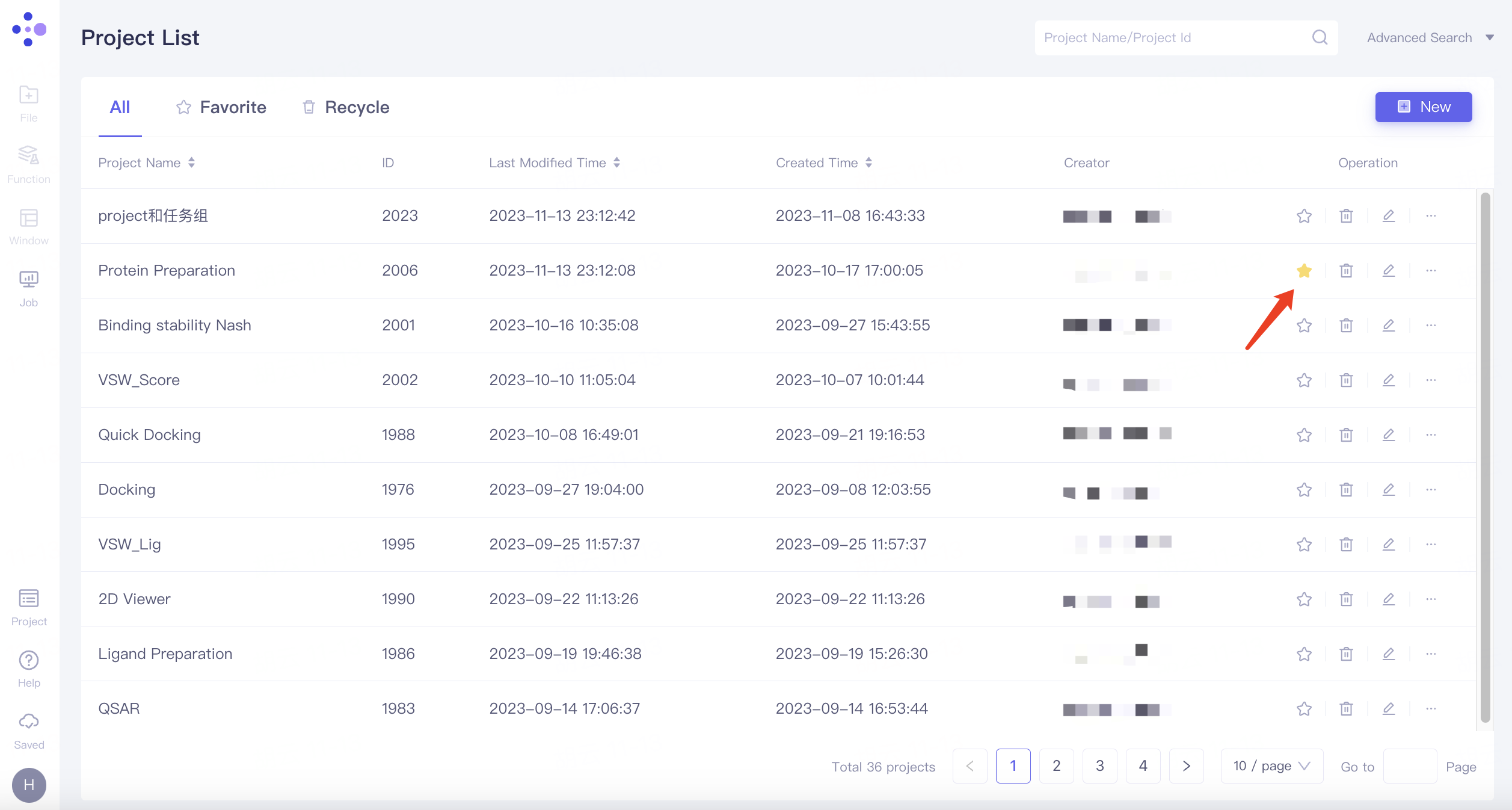
Project添加成员
当项目需要多人参与时,可通过如下方式实现项目在多人间的共享,具体操作如下:
管理员分享项目
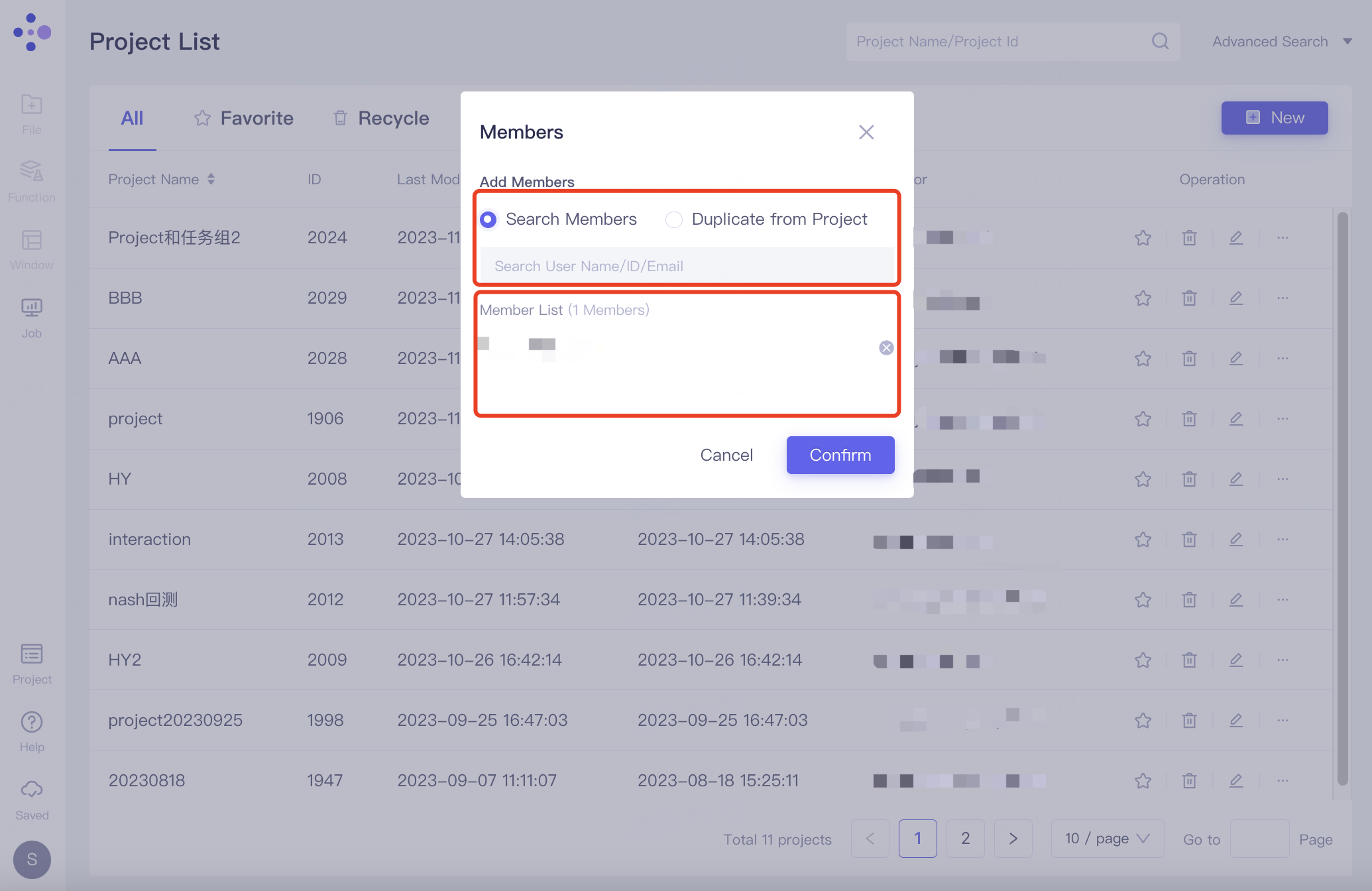
在展开的项目列表中找到需要分�享的项目,点击右侧Operation下的“...”,展开的选项中点击“Member”。
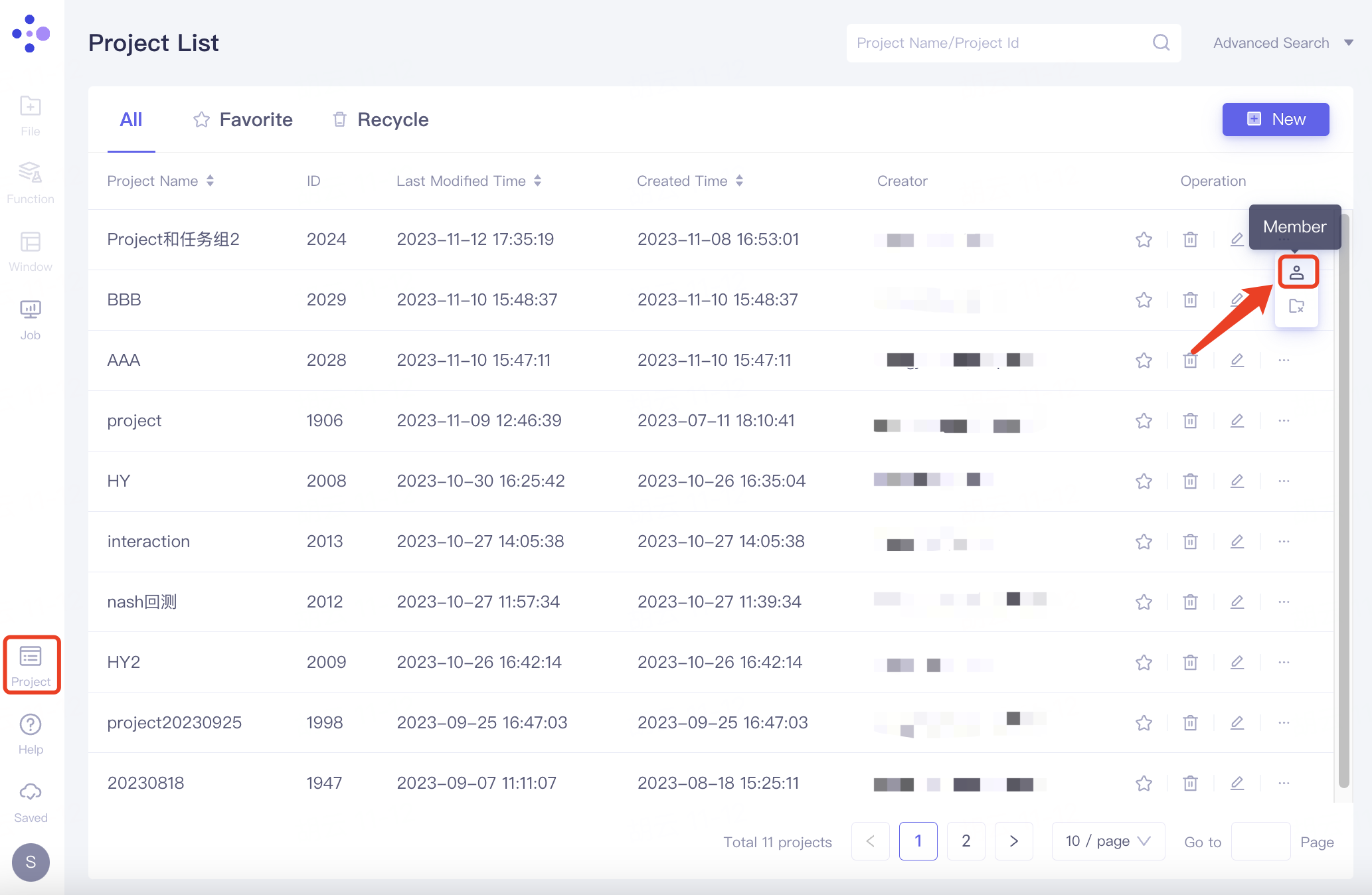
弹出“Members”界面,添加成员后,成员邮箱展示于Member List下,点击“Confirm”确认添加;
可通过两种方式添加成员:
Search Members:通过搜索用户名称/ID/电子邮箱邀请用户进入当前项目中;
Duplicate from Project:根据用户的项目名称/ID邀请用户进入当前项目中。
注:只能添加已在组织内的成员,组织内添加成员详见 2.8.3 User Center。
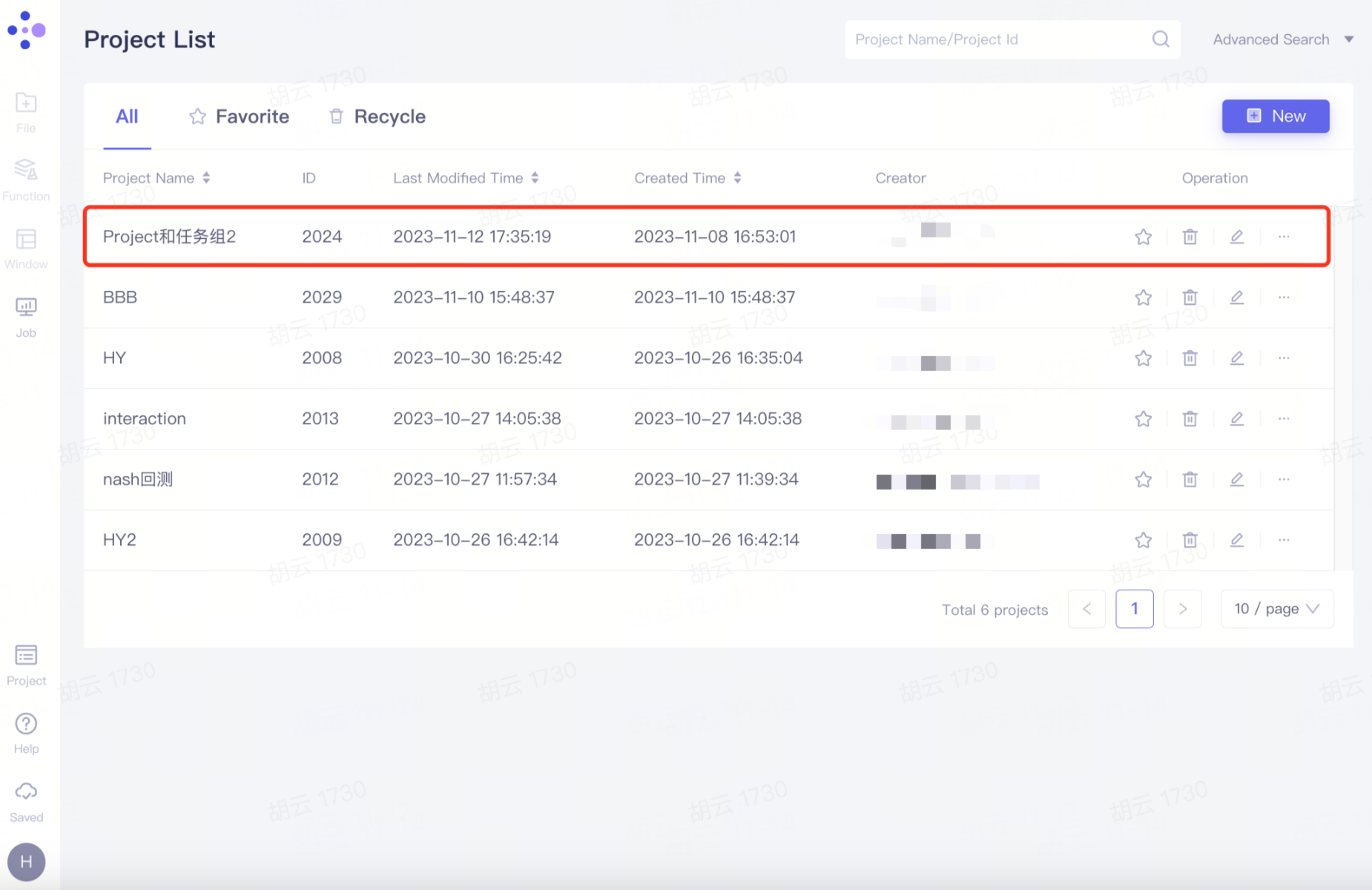
成员同步项目
成员账号中同步出现该项目
2.6 Help Center
帮助文档,包含首页、动态与公告、软件案例、操作手册、获取更多帮助。
2.7 Saving to the Cloud
将当前任务保存至云空间。
2.8 �账号中心
2.8.1 组织
当您未加入任何组织时,默认以您为管理员有一个独立的组织;当您加入组织后,可通过如下方式切换组织。
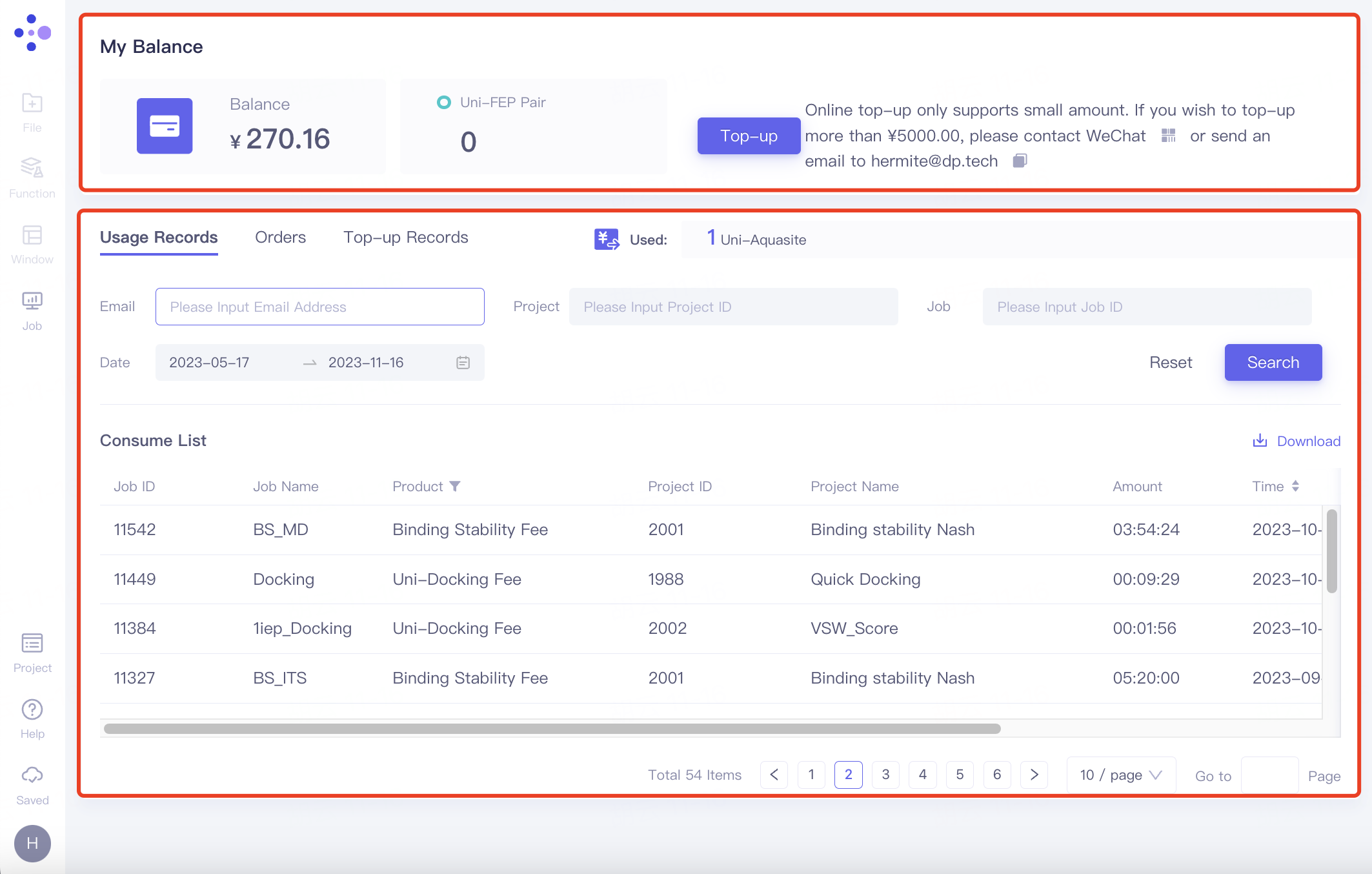
2.8.2 My Balance
上方红框处,Blance处所示为余额,Uni-FEP Pair处所示为剩余FEP Pair数目,点击“Top-up”可进行¥5000以内的小额充值。
下方红框处:
Usage Records:记录了资源包使用情况;
Orders:记录了资源包使用金额;
Top-up Records:充值记录。
2.8.3 User Center
用户中心界面中,上方为个人信息,下方User List记录着其他成员的信息
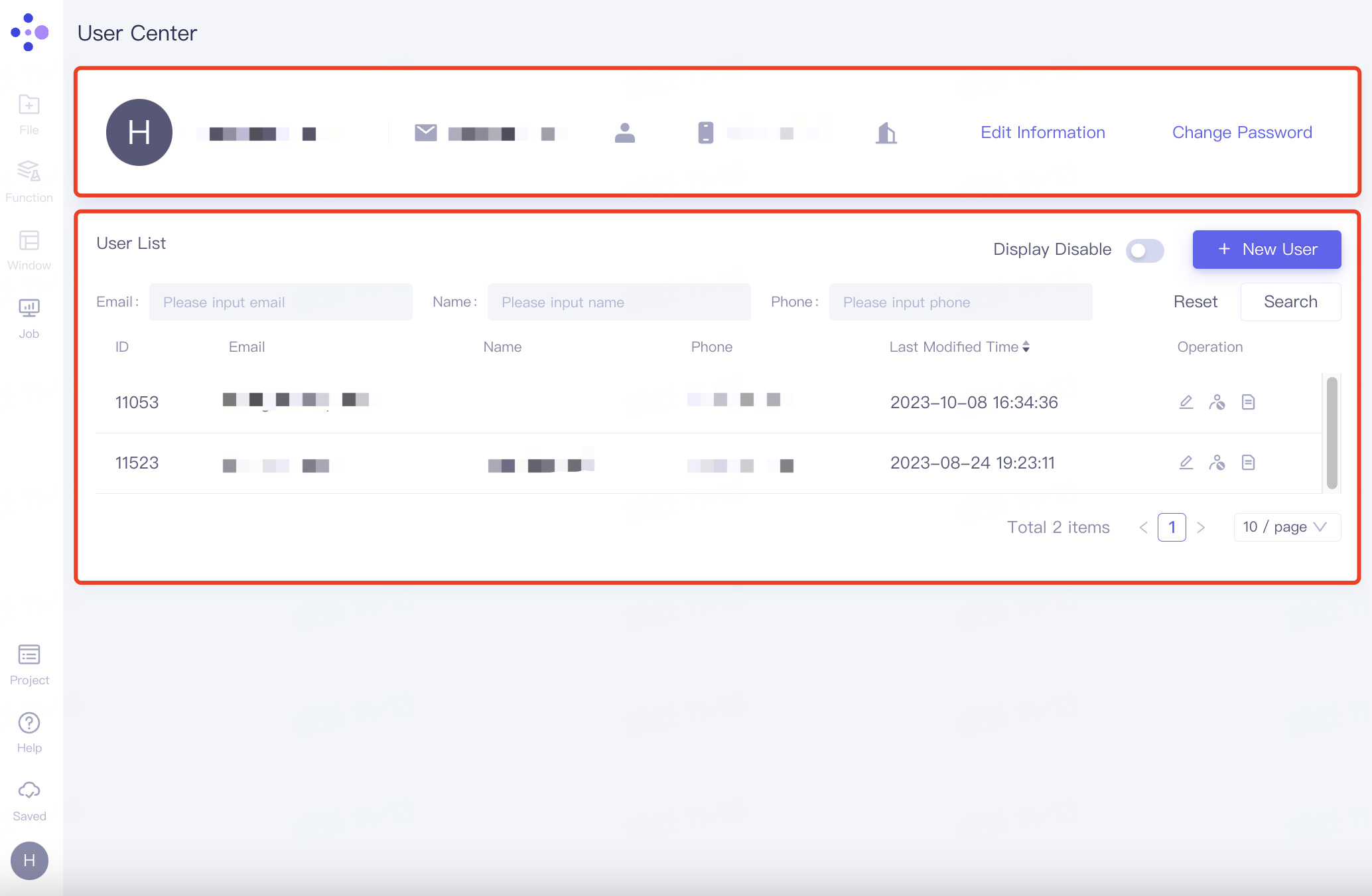
2.8.3.1 个人信息栏操作
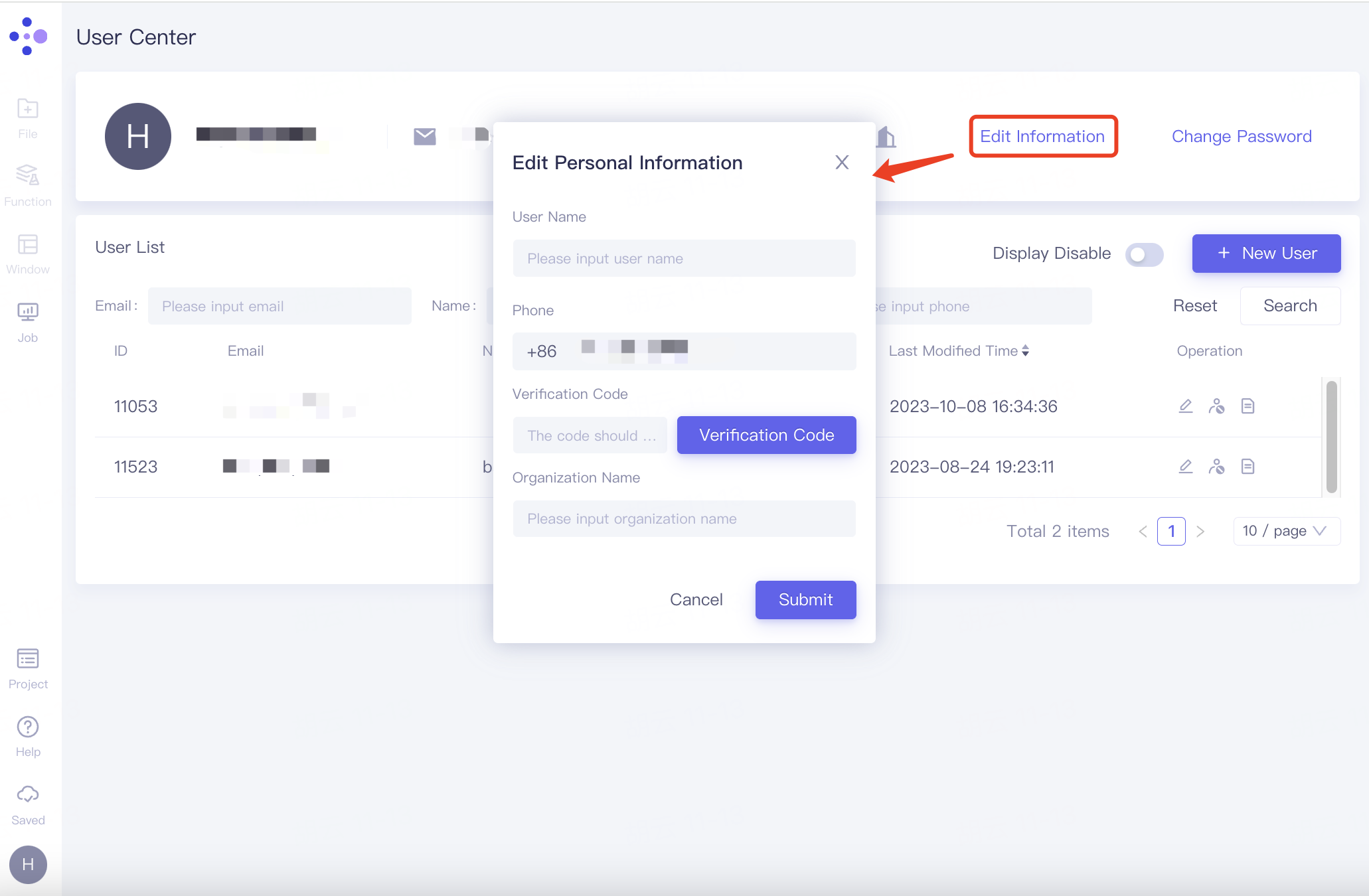
编辑个人/组织信息
在个人信息栏,点击右侧“Edit Information”,展开“Edit Personal Information”窗口。在下方填入用户名称、手机号、验证码及组织名称等信息,点击“Submit”。
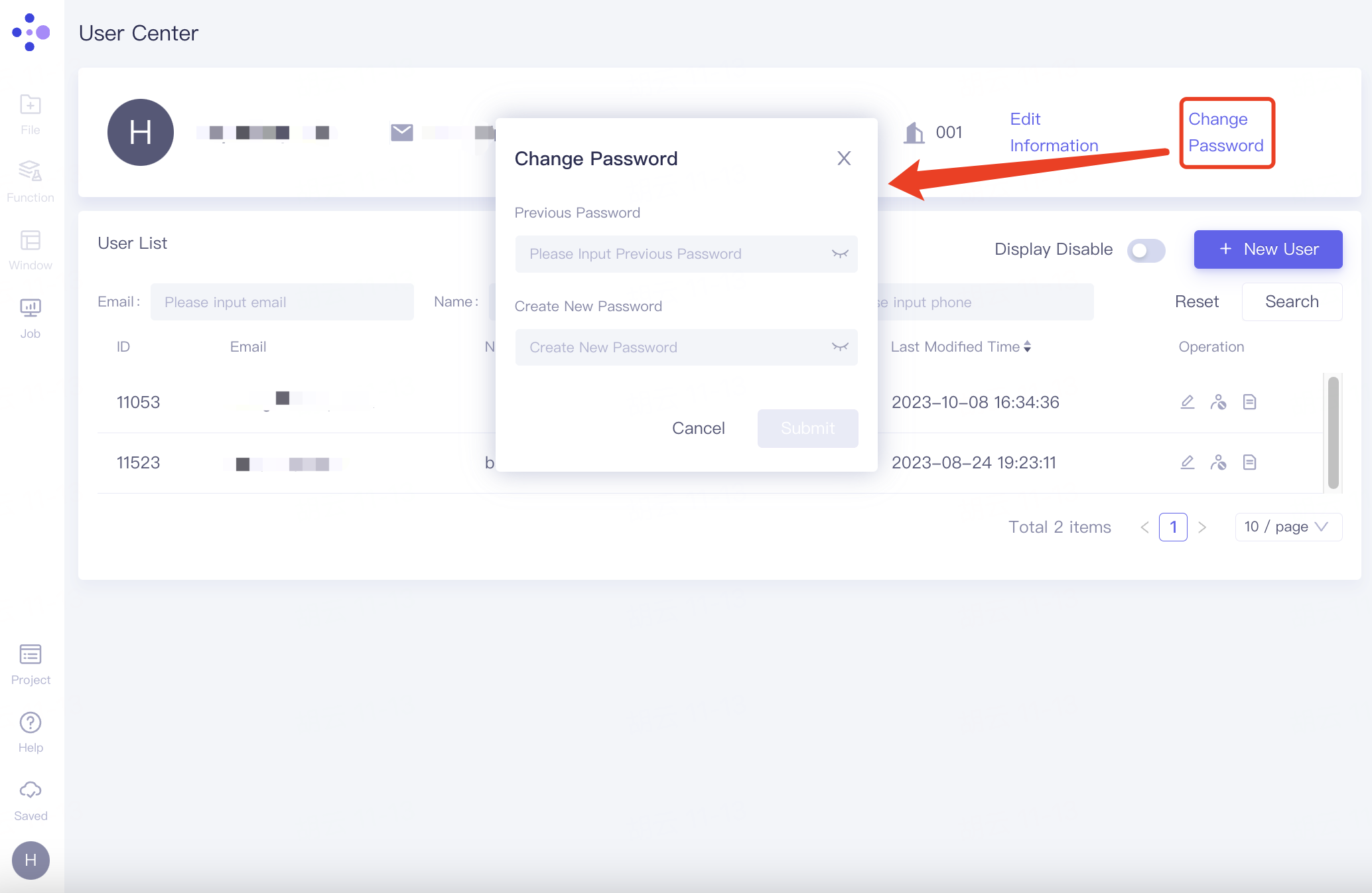
修改密码
在个人信息栏,点击右侧“Change Password”,弹出“Change Password”窗口,填入原始密码和修改后的密码,点击“Submit”。
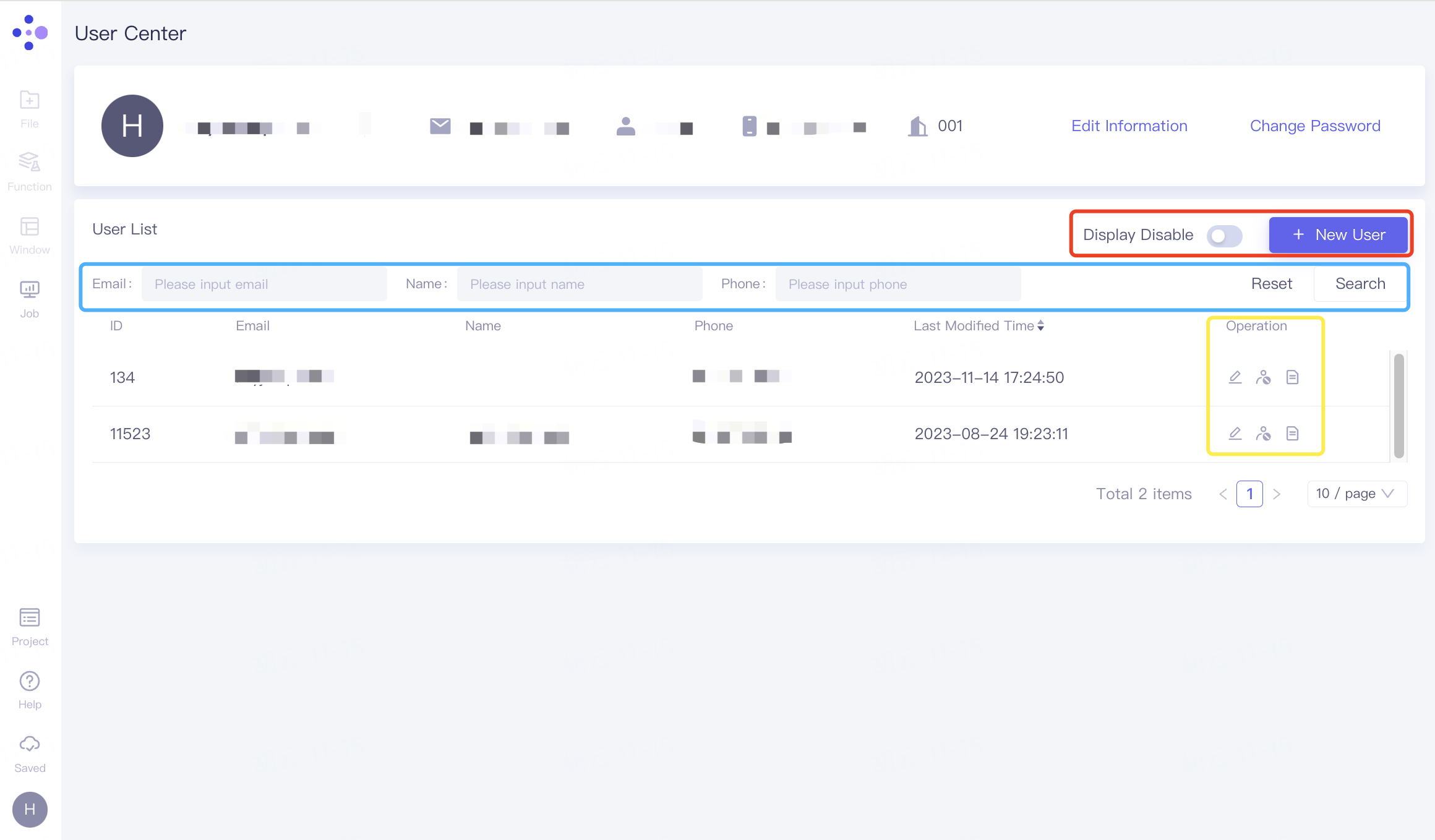
2.8.3.2 User List处操作
基本操作介绍
红框:
Display Disable:按钮可调整被禁止用户的显隐;
+New User:在当前组织内添加成员;
蓝框:根据Email、Name、Phone等信息,点击“Search”搜索所需用户,点击“Reset”可重置;
黄框:
Edit:调整该成员参与的Project;
Disable User:将成员从组织中删除;
Job Record:查看成员的任务记录。
组织管理
1)管理员邀请进入组织
点击账号,在展开的列表中选择“User Center”,进入用户中心
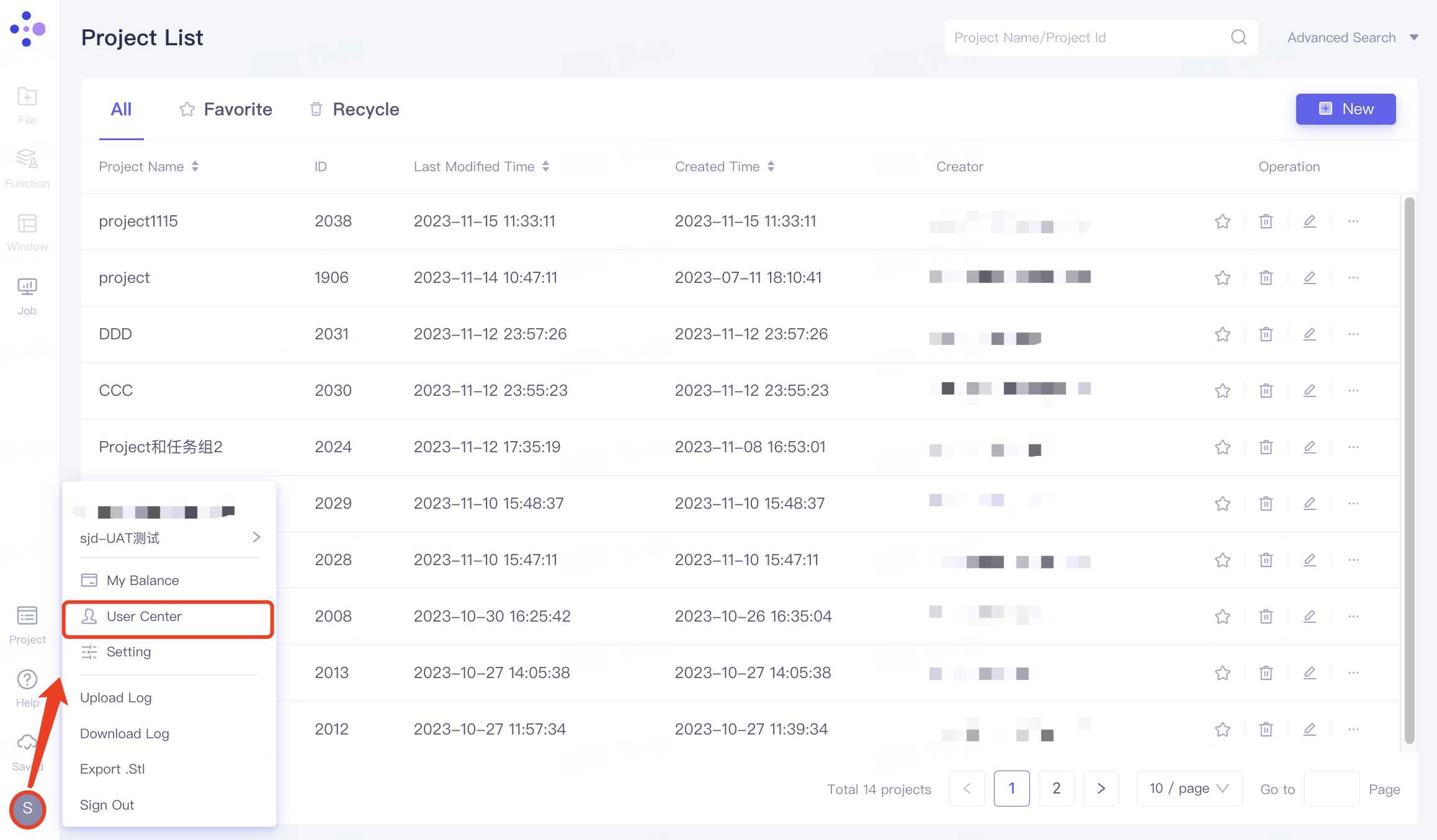
点击Edit Information,在弹出的窗口中,Organization Name处对该组织进行命名,点击“Submit”。
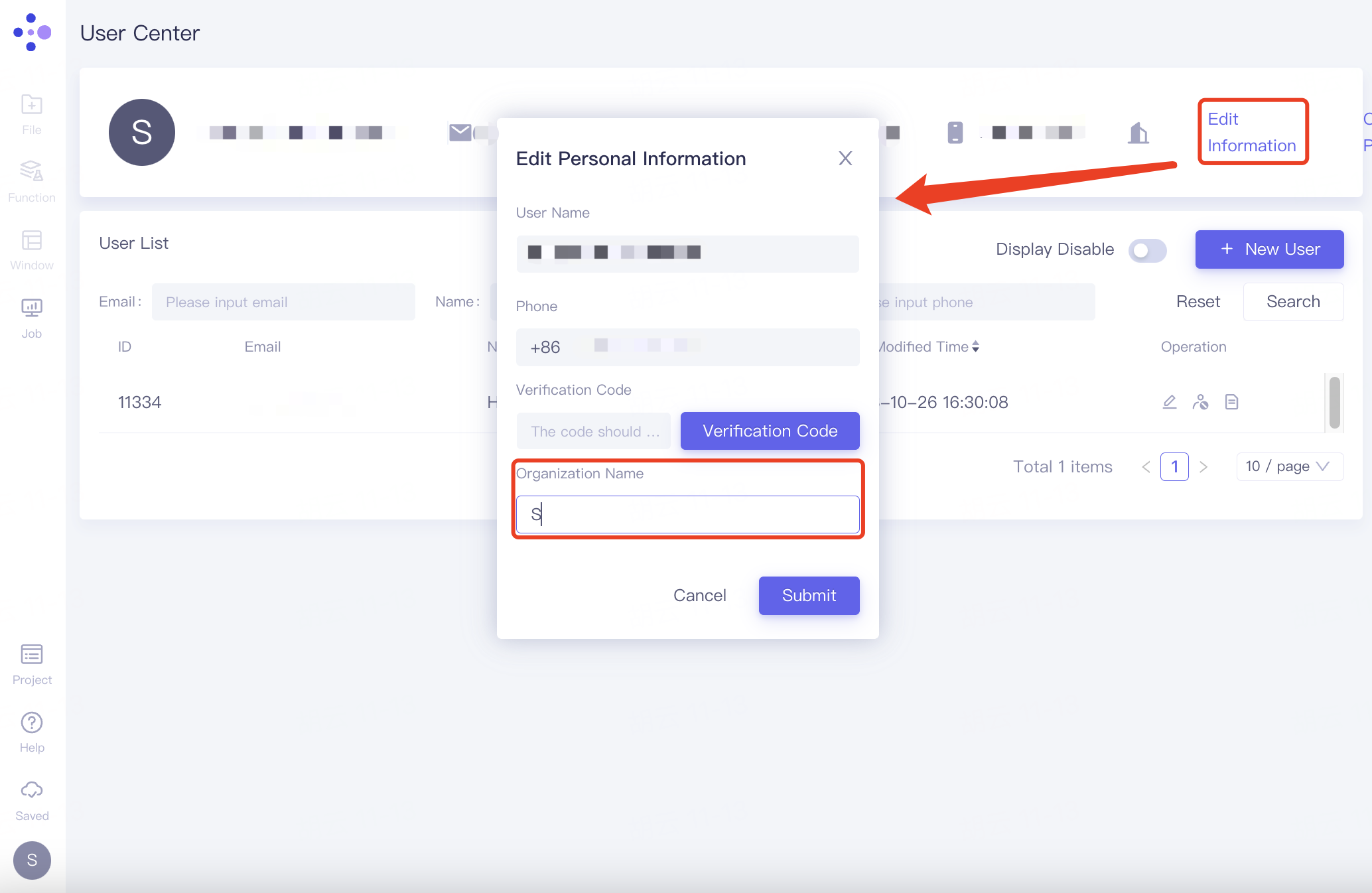
管理员通过“+ New User”邀请别人进入组织。点击“+ New User”,弹出“Edit User”窗口,在“*Email”处填写受邀人的邮箱,“Project”下选择可共享的项目,选择的项目会列于“Project List”下,点击“Submit”提交处理。
项目搜索与处理:
1)Search Projects:根据Project Name/ID搜索项目,下拉界面中出现符合条件的项目,点击即可使之载入Project List下;
2)Duplicate from Member:根据User Name/ID/Email搜索出某人员,下拉界面点击该人员即可在Project List列表中展现该人员的所有项目。
3)点击Project List右侧“All”,可使所有项目载入Project List下;
4)点击Project List右侧“Clear”,清除Project List下的所有项目。
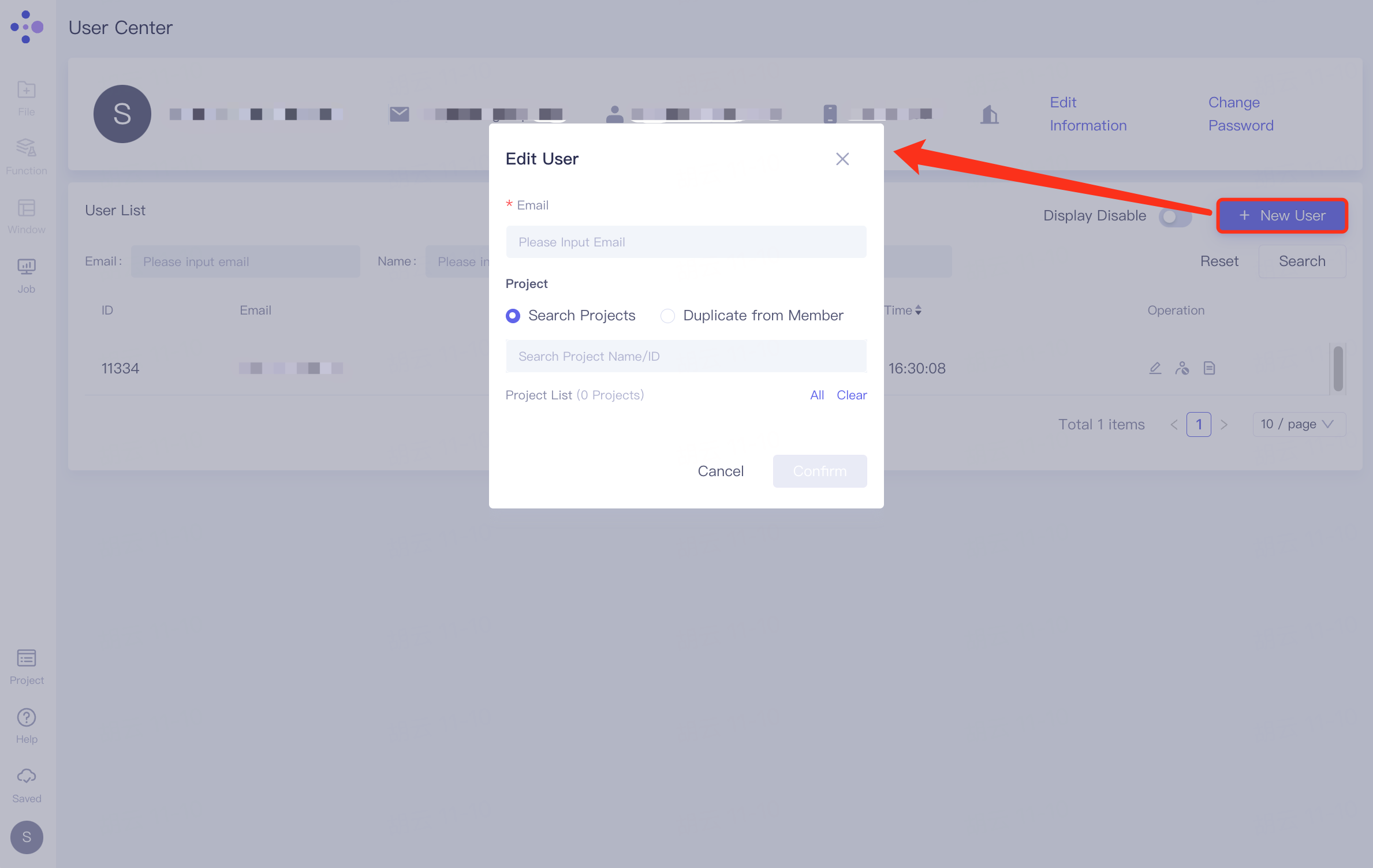
2)成员受邀加入组织
当管理员经过相关操作后,成员邮箱内会收到一封确认邮件,按照邮件提示进行操作;
登陆Hermite,点击账号,在展开的列表中邮箱号下面切换组织。
2.8.4 Setting
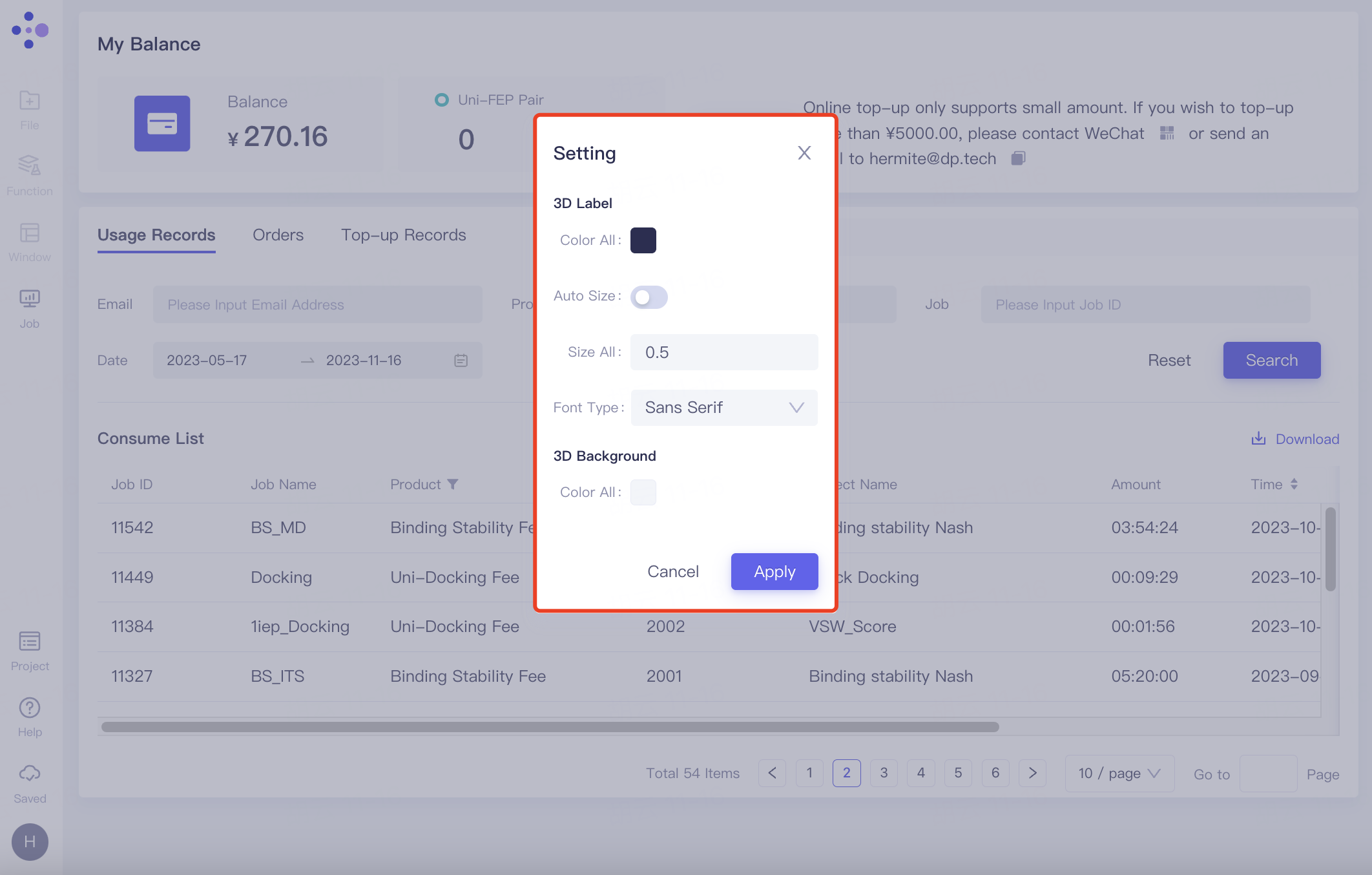
Setting:支持设置3D Workspace内的标签的颜色、尺寸、字体类型,以及3D Workspace界面的背景颜色。点击Apply即可更改设置。
2.8.5 Upload Log
上传日志。
2.8.6 Download Log
下载日志。
2.8.7 Export .Stl
导出为 .stl格式文件。
2.8.8 Sign Out
退出登录。